OpenZika близка к завершению работы над сетью мирового сообщества волонтеров
Community Grid за последние три года. Узнайте о следующих шагах для проекта в этом всеобъемлющем обновлении.
Завершение работы над сетью мирового сообщества
Недавно мы оценили работу, проделанную для проекта OpenZika, и пришли к выводу, что мы почти завершили то, что предложили, а именно провести виртуальный скрининг практически всех белков вируса Зика из самого большого набора данных доступных соединений (библиотека ZINC 15, содержащая приблизительно 30 миллионов соединений). Благодаря волонтерам, которые поддержали проект, у нас есть много, много результатов для оценки.
В течение следующих нескольких недель мы представим несколько дополнительных структур вируса Зика и полимеразы NS5 (РНК и активный сайт) и метилтрансферазы NS5 (сайт GTP), чтобы завершить наш проект. Когда группа разработчиков World Community Grid создает рабочие единицы для этих структур, это должно создать приблизительно 20 000 пакетов. Как только они будут завершены, мы полностью сосредоточимся на анализе данных.
Прогресс в выборе и тестировании соединений
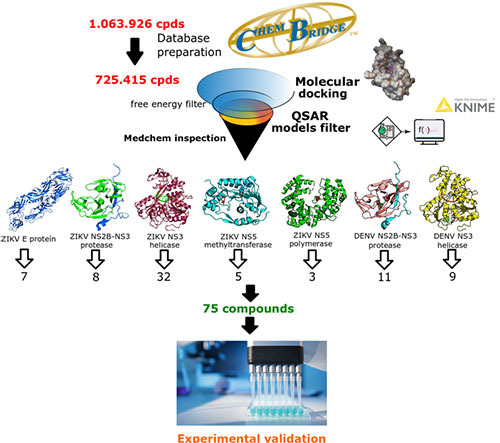
Мы фактически провели скрининг коммерческой базы данных ChemBridge, содержащей более 1 миллиона соединений, против белков вируса Зика (ZIKV): оболочки, протеазы, геликазы, полимеразы и метилтрансферазы.
Мы также проверили базу данных ChemBridge на наличие протеазы денге и протеазы геликазы. После расчета стыковки на OpenZika мы пропустили соединения через фильтр свободной энергии и фильтр моделей машинного обучения ZIKV. Мы также провели медицинский осмотр на основе наиболее перспективных кандидатов.
Этот новый раунд соединений позволил нам выбрать 55 новых кандидатов на вирус Зика и 20 кандидатов на лихорадку денге (рис. 1). Соединения были приобретены и отправлены в Калифорнийский университет в Сан-Диего в лаборатории доктора Джейра Сикейра-Нето для экспериментальной оценки. Они проводят клеточные анализы в нервных стволовых клетках человека (hNSCs) с ZIKV. Мы также проведем ферментные анализы в геликазе и протеазе белков ZIKV NS3 вместе с нашими сотрудниками в Физическом институте Сан-Карлоса, Университет Сан-Паулу (Бразилия), в лаборатории доктора Глауциуса Оливы, чтобы подтвердить действия предполагаемых ферментативных кандидатов.
271/5000
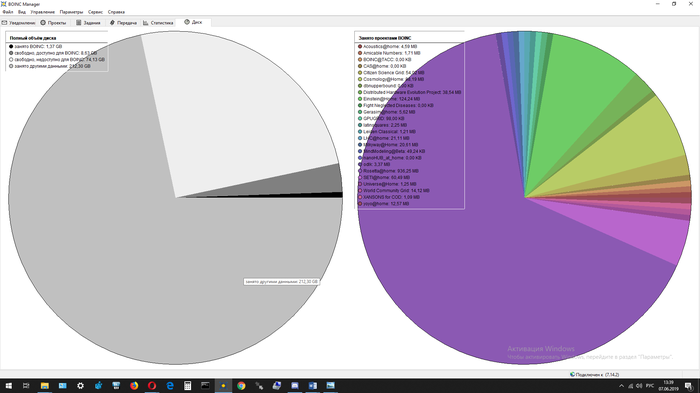
(Рис. 1. Ход экспериментов по виртуальному скринингу, выполненных для оболочки ZIKV (E), протеазы NS2B-NS3, геликазы NS3, полимеразы NS5 и метилтрансферазы NS5, а также для протеазы NS2B-NS3 DENV и геликазы NS3, с использованием базы данных ChemBridge (~ 1 миллион соединений).)
Кроме того, мы выполнили виртуальный скрининг двух собственных наборов данных о натуральных продуктах и полусинтетических соединениях от двух сотрудников: доктора Ластера из Университета штата Северная Каролина (Университет штата Северная Каролина) и доктора Регасини из Университета штата Сан-Паулу (Университет США). Мы фактически провели скрининг соединений против протеаз ZIKV NS3 и белков геликазы и пропустили соединения через фильтр свободной энергии. После этого мы выполнили целевой прогнозный анализ перспективных хитов. Затем экстрагированные и выделенные соединения были протестированы с использованием анализов in vitro, клеточных анализов и ферментативных анализов, чтобы подтвердить исследование in silico (рис. 2).
(Рисунок 2. Ход экспериментов по виртуальному скринингу, выполненных для протеазы ZIKV NS2B-NS3 и геликазы NS3, с использованием баз данных housenatural и полусинтетических соединений.)
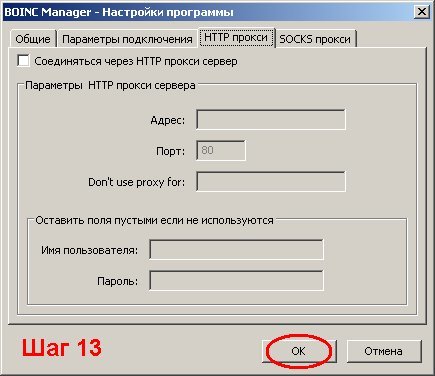
Состояние расчетов
В общей сложности мы предоставили почти 8,57 миллиарда рабочих мест для стыковки, в которых участвовало 427 различных целевых сайтов. На наших первых экранах использовалась более старая библиотека из 6 миллионов коммерчески доступных соединений, а в наших текущих экспериментах используется новая библиотека ZINC15 из 30,2 миллиона соединений.
К настоящему времени,> 80 000 добровольцев, которые пожертвовали свои запасные вычислительные мощности OpenZika, дали нам> 84 711 процессорных лет вычислений стыковки, в настоящее время в среднем 75,1 процессорных лет в день! Спасибо всем большое за вашу помощь !!
За исключением нескольких отставших, мы получили все результаты для наших экспериментов, которые включают стыковку 30,2 миллиона соединений против NS1, NS3 helicase (как сайта связывания РНК, так и сайта ATP), NS5 РНК-полимеразы (NTP и карман РНК), NS5 метилтрансфераза (сайт SAM), протеаза NS2B / NS3, капсид (карманы связывания 1 и 2) и белок оболочки.
Предстоящие публикации
Недавно мы опубликовали обзор под названием «Высокая пропускная способность и вычислительное перепрофилирование для забытых болезней» в журнале «Фармацевтические исследования». В этой статье описываются усилия по перепрофилированию многих лекарств, предпринимаемые в разных лабораториях по всему миру, чтобы попытаться найти способы лечения многих тропических заболеваний, включая инфекции Зика и денге.
Исследователи OpenZika Доктор Мелина Моттин, Доктор Рузвельт Сильва, Msc. Бруна Соуза и Пауло Рамос представили тезисы для рассмотрения для устной и / или постерной презентации на конференции 9thBrazMedChem2019, крупнейшей конференции по медицинской химии в Латинской Америке. Д-р Моттин и Бруна представят исследования, связанные с природными соединениями: «Открытие флавоноидов из нитроген птерогина с мощной активностью против протеазы и геликазы вируса Зика» и «Открытие новых кандидатов на вирус Зика: натуральные продукты из Angelica keiskei с активностью против NS2B- Протеаза NS3». Пауло представит работу «Интегративный анализ сходства, модели стыковки и машинного обучения для выявления новых хитов Zika NS5, управляемых ингибиторами денге NS5». Доктор Рузвельт представит исследование молекулярной динамики ZIKV NS1: «Динамическое поведение денге и Белок NS1 вирусов Zika раскрывает механизмы взаимодействия мономер-мономер и дает представление о рациональном дизайне лекарств».
Документы в стадии написания - будут представлены в ближайшее время:
Мы готовим следующие статьи о впечатляющих результатах проекта OpenZika:
В одной статье сообщается о результатах (виртуальных и экспериментальных) первого раунда соединений, отобранных против геликазы ZIKV NS3, которые продемонстрировали анти-ZIKV-активность в нервных стволовых клетках человека (hNSC)
В трех работах сообщалось о замечательных результатах виртуального скрининга и экспериментальной оценки натуральных продуктов (две из коллаборации Бразилии и одна из коллаборации NC State University), растений из Бразилии и традиционной китайской медицины, соответственно, которые представили анти-ZIKV активность, ингибирующую ZIKV протеины протеазы и / или геликазы
В одном документе сообщается о результатах для утвержденных лекарственных препаратов / соединений клинических коллекций, которые обладают противомалярийной и противоболевой активностью, которые представили анти-ZIKV-активности против белка геликазы ZIKV, кандидатов на повторное использование лекарственных средств.
В одной статье представлены результаты расчетов моделирования молекулярной динамики белка ZIKV NS1 и сведения о связывающих карманах и дизайне лекарств. Эта статья была представлена в Журнал биомолекулярной структуры и динамики под названием «Динамическое поведение вирусов Денге и Зика. Белок NS1 раскрывает механизмы взаимодействия мономер-мономер и дает представление о рациональном дизайне лекарств», и в настоящее время рассматривается для публикации.
Команда также совместно подготовила главу для книги по трипаносомным болезням, которая будет опубликована в журнале Burger's Medicinal Chemistry.
Эти документы будут вскоре представлены в научных журналах.
Прошлые публикации и пропаганда
20 июня 2018 года был опубликован основной обзор «Обнаружение наркотиков сегодня» «Обнаружение лекарств от А до Я». Это всеобъемлющий обзор недавних достижений в области обнаружения наркотиков ЗИКВ, в котором освещаются репозиционирование лекарств и соединения с компьютерным контролем, в том числе недавно обнаруженные вирусные. и ингибиторы клетки-хозяина. Также описываются и обсуждаются перспективные молекулярные мишени ZIKV, а также мишени, принадлежащие клетке-хозяину, как новые возможности для открытия лекарств ZIKV. Все эти знания важны не только для продвижения борьбы с вирусом Зика и другими флавивирусами, но также помогут научному сообществу подготовиться к следующей новой вирусной вспышке, на которую нам придется реагировать.
Наша статья «Вычисление лекарств для вируса Зика» была опубликована в специальном выпуске Бразильского журнала фармацевтических наук. В этой статье мы кратко излагаем текущие усилия по поиску вычислительных лекарств и их применение для обнаружения лекарств против ZIKV. Мы также представляем успешные примеры использования вычислительных подходов к открытию лекарств ZIKV, включая наш проект OpenZika.
Д-р Шон Экинс представил плакат «Клеточные симпозиумы: новые и вновь возникающие вирусы» 1-3 октября 2017 года в Арлингтоне, штат Вирджиния, США, под названием «OpenZika: открытие новых противовирусных кандидатов против вируса Зика».
20 октября 2016 года была опубликована наша статья о забытых тропических заболеваниях PLoS «OpenZika: проект всемирного сетевого сообщества IBM по ускорению обнаружения вируса Зика», и ее уже просмотрели более 5200 раз. Любой может получить доступ и прочитать эту статью бесплатно. Другой исследовательский документ «Иллюстрирование и моделирование гомологии белков вируса Зика» был опубликован в F1000Research и просмотрен> 4200 раз.
Мы также опубликовали еще одну исследовательскую работу под названием «Моделирование молекулярной динамики геликазы Zika Virus NS3: анализ активности сайтов связывания РНК» в специальном выпуске по флавивирусам для журнала Biochemical and Biophysical Research Communications. Это исследование системы геликазы NS3 помогло нам узнать больше об этой многообещающей цели для блокирования репликации Zika. Результаты помогут нам понять, как мы анализируем виртуальные экраны, которые мы выполняли на геликазе NS3, и моделирование молекулярной динамики создало новые конформации этой системы, которые мы использовали в качестве мишеней на новых виртуальных экранах, которые мы выполняли в рамках OpenZika.
Результаты проекта OpenZika были представлены на 256-м Национальном собрании ACS 19-23 августа 2018 года в Бостоне, штат Массачусетс, США. Доктор Моттин выступил с устной презентацией и представил плакат под названием «OpenZika: открытие новых противовирусных кандидатов против вируса Зика»; в сессии «Хемоинформатические подходы для улучшения обнаружения лекарств на основе натуральных продуктов».
Д-р Моттин также выступил с устной презентацией «Применение молекулярной динамики к обнаружению лекарств для вируса Зика и Schistosoma mansoni» на встрече по инициативе Южной Америки по сотрудничеству в области молекулярного моделирования (SAIMS), которая состоялась в Институте Пастера, Монтевидео, Уругвай, 4 ноября. 7, 2018. Встреча была отличной возможностью для обмена опытом и сотрудничества с южноамериканскими исследователями, которые работают с Zika.
Информация о БразМедХим
Главный исследователь OpenZika, профессор Каролина Орта Андраде, также директор Отдела медицинской химии Бразильского химического общества (SBQ), организует крупнейшую конференцию по лекарственной химии и открытиям лекарств в Латинской Америке, 9thBrazMedChem2019, которая состоится 1 сентября -4, 2019, в Пиренополисе, Гояс, Бразилия.
Основная тема конференции этого года - «Преодоление разрыва между академической и фармацевтической промышленностью в продвижении открытия лекарств». Оргкомитет и научные комитеты работают над тем, чтобы сохранить выдающееся качество прошлых изданий, пытаясь обеспечить эффективное вовлечение и участие научного сообщества в современной структуре, которая объединяет научные и социальные мероприятия высокого уровня для объединения участников.
Мы рассчитываем принять около 500 человек, в основном аспирантов, исследователей и профессоров, работающих в области медицинской химии из Бразилии и стран Латинской Америки, в интерактивной и совместной атмосфере для обмена опытом и информацией для решения задач медицинской химии 21 век.
Более того, доктор Шон Экинс, коллега по проекту OpenZika, едет в компанию 9thBrazMedChem, чтобы рассказать о нашей работе над OpenZika, а также о работе над болезнью Шагаса и открытием лекарств от Эболы, которая представляет собой лишь некоторые из забытых болезни, с которыми он связан.
Новые члены команды проекта
Пауло Рамос - новый студент, который присоединился к лаборатории профессора Андраде в январе 2019 года. В своей проектной работе он впервые искал ингибиторы NS5 вируса денге в базах данных PubChem и ChEMBL. Он также выполнил интегративный анализ сходства белков денге и Zika NS5, закрепление известных ингибиторов DENV на сайтах Zika NS5 и модели машинного обучения (ML) для определения приоритетов лучших результатов. Он обнаружил 156 соединений, о которых сообщалось, что они являются ингибиторами денге NS5, которые были закреплены на сайтах Zika NS5 и оценены моделями ML. Двадцать два соединения были отобраны как демонстрирующие наилучшие результаты. Затем он выполнил аналогичный поиск с попаданиями в коммерческую базу данных (электронные молекулы) и проверил похожие соединения с помощью стыковочных и ML-фильтров. 67 виртуальных хитов для Zika NS5 будут проверены с помощью клеточных тестов Zika.
(Команда OpenZika LabMol: Мелина, Каролина, Бруна и Пауло в лаборатории в Федеральном университете Гояс, Бразилия (весна 2019 г.))
(Сотрудничество Pharmeceuticals (слева направо): Шон Экинс, Дэниел Фоил, Кимберли Цорн, Ана Пухл Рубио, Дженнифер Кляйн, Мэгги Хапси, Томас Лейн, Андреа Барри (бизнес-консультант))
В лаборатории д-ра Экинса Ким и Дэниел (см. выше) участвовали в оценке соединений для проектов OpenZika с нашими моделями машинного обучения, разработанными для разных наборов данных. Сотрудничество Фармацевтические препараты продолжают бороться с забытыми болезнями, сотрудничая с учеными всего мира. Если вы заинтересованы в сотрудничестве с нами, пожалуйста, свяжитесь с sean@collaborationspharma.com.
Мы невероятно благодарны всем волонтерам, которые тратят свое неиспользованное компьютерное время на этот проект! Большое спасибо!!
https://link.springer.com/article/10.1007%2Fs11095-018-2558-...
https://brazmedchem.org/
https://doi.org/10.1016/j.drudis.2018.06.014
http://www.scielo.br/pdf/bjps/v54nspe/2175-9790-bjps-54-spe-...
http://www.cell-symposia.com/emerging-viruses-2017/
http://journals.plos.org/plosntds/article?id=10.1371%2Fjourn...
https://f1000research.com/articles/5-275/v1
http://www.sciencedirect.com/science/article/pii/S0006291X17...
http://www.acs.org/bostoninfo